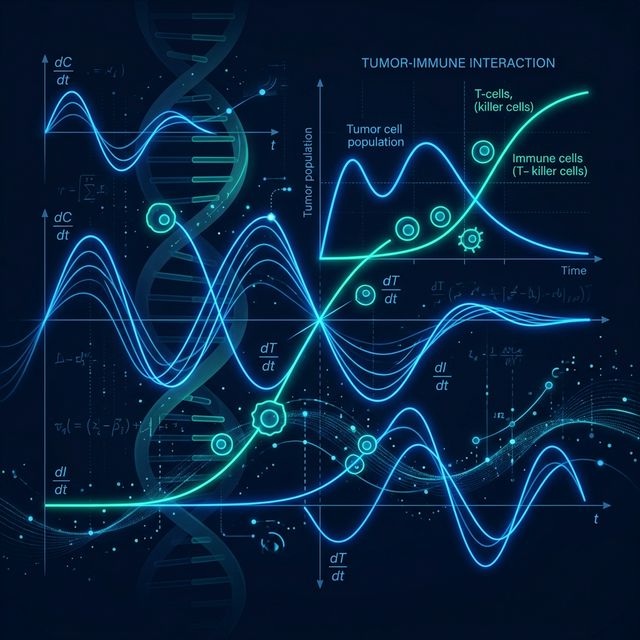
Modèle de Dynamique Tumeur-Système Immunitaire
01. Vue d'ensemble
Plateforme web interactive pour explorer le modèle mathématique NTIUNHDM et les interactions complexes entre cellules tumorales, réponse immunitaire et facteurs nutritionnels.
Objectif
Rendre accessibles des mathématiques complexes de recherche sur le cancer via des visualisations interactives et des simulations en temps réel.
Résultat
Une plateforme de recherche interactive combinant modélisation rigoureuse et simulation intuitive pour chercheurs, étudiants et public.
02. Stack technique
03. Fonctionnalités clés
Simulation cellulaire interactive en temps réel (cellules normales, tumorales et immunitaires)
Explorateur d'équations différentielles avec paramètres ajustables
Visualisation interactive des résultats de recherche
Comparaison de solveurs EDO et analyse d'erreurs
Bascule mode clair/sombre
Design entièrement responsive
04. Pipeline d'ingénierie
Étude du papier NTIUNHDM et traduction des équations en solveurs numériques
Conception de composants React modulaires pour chaque section (équations, résultats, code)
Intégration de Framer Motion pour des transitions fluides et des animations pilotées par les données
Déploiement sur Vercel avec intégration continue via GitHub
05. Défis & exécution
Contrainte
Visualiser en temps réel le comportement d'équations différentielles complexes
Exécution
Création d'un moteur d'animation Canvas personnalisé pour visualiser les interactions cellulaires en direct.
Contrainte
Rendre accessibles des mathématiques avancées de recherche sur le cancer
Exécution
Intégration de MathJax pour un rendu clair des équations avec des explications en langage simple.
Contrainte
Représenter fidèlement la dynamique multi-variables des populations cellulaires sur canvas
Exécution
Ajout de curseurs interactifs pour observer l'effet des paramètres sur les équilibres tumeur-immunité.